Mettez en évidence les variantes cliniquement exploitables grâce au filtre
Pour accélérer le processus de production de rapports, nous intégrons de manière unique la base de données des variantes N-of-One ou votre propre base de connaissances organisée nativement sur la plate-forme. Cette intégration permet de faire apparaître des variantes cliniquement exploitables par filtrage pour une sélection rapide.
Mettez en évidence, annotez, filtrez et établissez des priorités
de données génomiques les plus complètes au sein même d’IntelliSpace Genomics. Elle s’ajoute à toutes les sources de données publiques disponibles que la plate-forme propose pour permettre des annotations complètes, un filtrage et une définition fiable des priorités.
Notre intégration unique avec N-of-One combine l’une des bases

Que signifie l’intégration avec N-of-One ?
“Leader incontesté dans le domaine de l’informatique clinique, Philips intègre et gère des Big Data dans les environnements médicaux”, a déclaré Chris Cournoyer, PDG de N-of-One. “Nous pensons que l’intégration de la base de données des variantes N-of-One et de ses services d’analyse et d’interprétation des dossiers patient sera rendue possible grâce à une intégration étroite avec cette solution de santé numérique de pointe.”
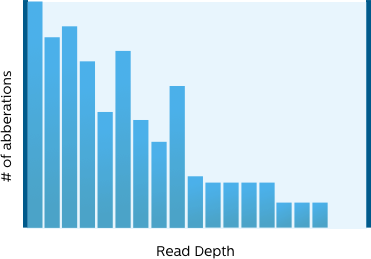
Options de filtrage intuitif
Pour mettre l’accent sur les informations et/ou les variantes exploitables parmi le grand nombre de cas détectés par NGS, nous proposons des options de filtrage visuel et flexible. Pour faciliter l’accès aux filtres, nous les avons classés selon le CQ, la fréquence, les scores d’impact fonctionnel et les catégories de présence dans la base de données. Notre interface de filtrage visuel affiche la distribution des variantes en fonction de la profondeur de lecture et de la fréquence des allèles afin que vous puissiez optimiser vos filtres en un coup d’œil.